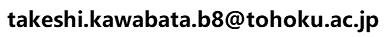
がん化した細胞からは非常に多数の変異部位が観察されるため、その中から機能的に重要な部位を抽出することが重要となります。このページでは、HOMCOSとPyMOLのスクリプトpy3Dcluster.pyを利用して、蛋白質の立体構造上集積している変異部位(3D cluster)から、潜在的ながん関連部位(potential cancer-associated sites)を認識する方法を説明します。3D clusterの認識法はGao et al, 2017に基づいています。


>PyMOLの行に), read_mutations([mutation_file])のように打ち込む。この場合、[mutation_file]は、"KEAP1_ProteinChange.tsv"なので、read_mutations("KEAP1_ProteinChange.tsv")と打ち込む。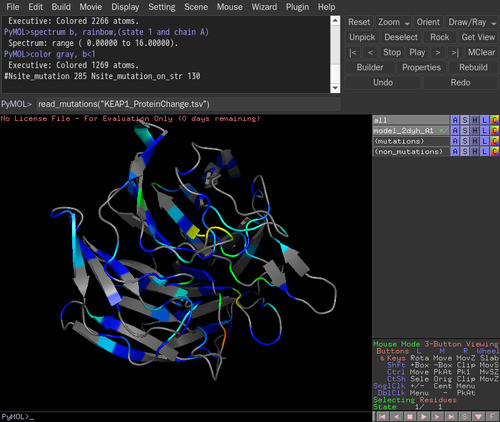
>PyMOLの行)に, cal_3Dcluster()と打つ。3Dクラスタの変異数とは、コンタクトしている周辺残基の変異数の和である。もしどれかの原子ペアが5Å以内にあれば、二つの残基はコンタクトしているとみなす。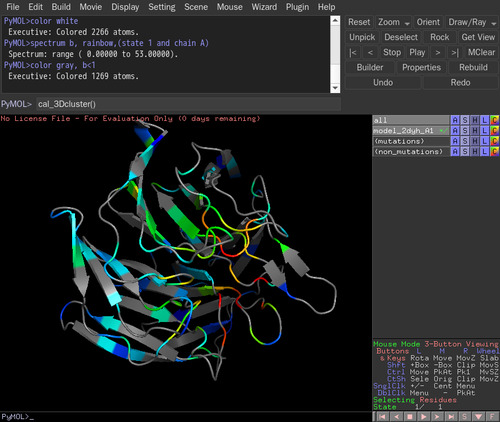
cal_3Dpvalue()と打つ。残基番号をランダムにN回シャッフリングして、3Dクラスタの変異数を再計算し、もとの3Dクラスタの変異数を何回上回るか計算する。その数をNで割った値がp値である。Nのデフォルトの値は100000である。cal_3Dpvalue(N=100)などと打つとNの値を変更することができる。
cal_asa()と打つ。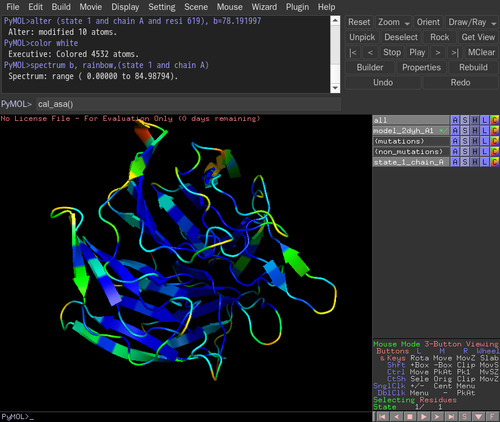
select_3Dpvalue()と打つ。p値のデフォルトは0.05である。p値の低い残基は"3Dp0.05"という名称が付く。p値の値は、select_3Dpvalue(p=0.01)などと打つことで変更できる。
select_neighbor(selection="3Dp0.05")と打つ。距離のしきい値は6Å.。選択された残基は "3Dp0.05n6"という名称となる。距離のしきい値は select_neighbor(selection="3Dp0.05",Dthre=8)などと打つと変更できる。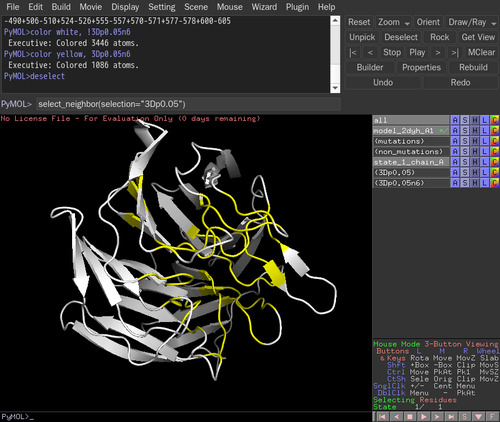
select_neighbor_surf(selection="3Dp0.05")と打つ。デフォルトの相対露出面積(relative ASA)は20 %である。選択された残基は"3Dp0.05n6s20"という名称になる。相対露出面積(%)の値は、select_neighbor_surf(selection="3Dp0.05",relasa=30)などと打つと変更できる。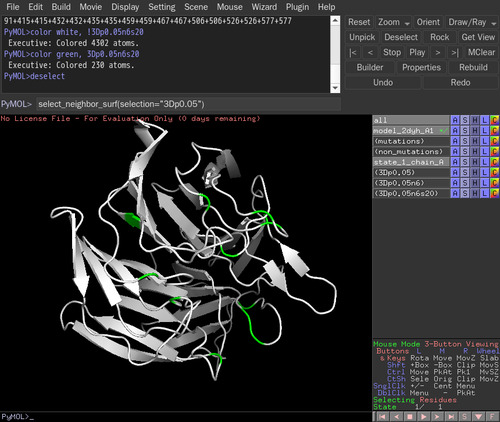
write_selection("3Dp0.05n6s20.txt",selection="3Dp0.05n6s20")と打ち込む。出力ファイル名は"3Dp0.05n6s20.txt"である。他の選択された残基も write_selection("3Dp0.05.txt",selection="3Dp0.05") やwrite_selection("3Dp0.05n6.txt",selection="3Dp0.05n6")などと打つことによって出力することができる。 
>> 3Dp0.05n6s20.txt <<
#write_selection(ofname='3Dp0.05n6s20.txt',selection='3Dp0.05n6s20') #COMMAND pymol_3Dcluster.py #DATE 2021/05/16 14:13:55 #MIN_RELASA 20.000000 MIN_MINDIS_FRM_SELECTED 6.000000 #FOCUS_MODEL 1 FOCUS_CHAIN A #[chain:1] [resi:2] [resn:3] #[MINDIS_FRM_SELECTED(A):4] [RELASA(%):5] #[count_mutation:6] [cluster3D(mutation_density):7] #[pvalue_cluster3D:8] [-log(pvalue_cluster3D):9] #[contact_residues:10] A 334 TYR 20.33 3.78 0 0 -1.000000 -1.000000 332 333 335 336 337 338 339 363 382 577 600 601 602 603 A 335 PHE 29.51 5.20 1 26 +0.081920 +1.086610 333 334 336 337 339 577 600 601 A 341 TYR 20.68 5.15 0 0 -1.000000 -1.000000 330 331 332 339 340 342 343 354 357 358 599 601 A 391 SER 22.19 5.95 0 0 -1.000000 -1.000000 378 389 390 392 393 408 409 411 412 413 A 415 ARG 21.00 0.00 6 50 +0.002120 +2.673664 364 379 413 414 416 417 430 431 461 462 463 508 509 556 A 432 HIS 32.80 3.81 0 0 -1.000000 -1.000000 389 411 412 430 431 433 434 435 437 A 435 ILE 42.32 5.62 0 0 -1.000000 -1.000000 430 431 432 433 434 436 437 461 A 459 ARG 47.35 3.82 1 17 +0.297920 +0.525900 436 437 438 456 457 458 460 461 478 479 484 A 467 VAL 23.18 4.59 0 0 -1.000000 -1.000000 419 420 421 465 466 468 469 470 471 472 473 514 A 506 ILE 20.19 3.81 1 13 +0.472110 +0.325957 483 484 485 503 504 505 507 508 525 526 531 A 526 ASP 22.43 4.97 0 0 -1.000000 -1.000000 483 505 506 507 524 525 527 528 529 531 A 577 PHE 20.52 5.05 0 0 -1.000000 -1.000000 334 335 571 572 575 576 578 579 600 601 602 A 334 TYR 20.33 3.78 0 0 -1.000000 -1.000000 332 333 335 336 337 338 339 363 382 577 600 601 602 603 A 335 PHE 29.51 5.20 1 26 +0.081920 +1.086610 333 334 336 337 339 577 600 601 A 341 TYR 20.68 5.15 0 0 -1.000000 -1.000000 330 331 332 339 340 342 343 354 357 358 599 601 A 391 SER 22.19 5.95 0 0 -1.000000 -1.000000 378 389 390 392 393 408 409 411 412 413 A 415 ARG 21.00 0.00 6 50 +0.002120 +2.673664 364 379 413 414 416 417 430 431 461 462 463 508 509 556 A 432 HIS 32.80 3.81 0 0 -1.000000 -1.000000 389 411 412 430 431 433 434 435 437 A 435 ILE 42.32 5.62 0 0 -1.000000 -1.000000 430 431 432 433 434 436 437 461 A 459 ARG 47.35 3.82 1 17 +0.297920 +0.525900 436 437 438 456 457 458 460 461 478 479 484 A 467 VAL 23.18 4.59 0 0 -1.000000 -1.000000 419 420 421 465 466 468 469 470 471 472 473 514 A 506 ILE 20.19 3.81 1 13 +0.472110 +0.325957 483 484 485 503 504 505 507 508 525 526 531 A 526 ASP 22.43 4.97 0 0 -1.000000 -1.000000 483 505 506 507 524 525 527 528 529 531 A 577 PHE 20.52 5.05 0 0 -1.000000 -1.000000 334 335 571 572 575 576 578 579 600 601 602
mk_dic_resn_frm_resi_from_get_model()
translate_mutation_resi_list_from_string(sites_string)
make_resi_list_on_structure(resi_list)
make_pymol_select_str_from_resi_list(resi_list)
mk_decimal_string(x)
random_permutation_list(array)
sort_num_str_list(str_list)
LastModfied:2023/01/31
質問/コメント: